魏文胜课题组报道新型线粒体碱基编辑器
线粒体作为细胞的"能量中心"在细胞生命活动过程中扮演着重要角色,它还是细胞核外存储遗传信息的另一细胞器。据MITOMAP数据库统计,在已确认的97种线粒体遗传疾病中,93种由点突变引起,因此使用碱基编辑工具修正这些突变具有重要意义。然而线粒体中的电子传递将质子从线粒体基质排出,使得基质带有强负电荷,这阻碍了具有相同负电荷核酸(如CRISPR系统的sgRNA)的进入1。全蛋白基础的基因编辑工具ZFN和TALEN可以在定位信号的引导下进入线粒体,之前有研究报道在小鼠线粒体中可以据此靶向敲低突变的基因组2,3。然而,敲低线粒体基因组不能治疗纯合的线粒体突变,也不能主动改变线粒体基因组的碱基构成。
基于CRISPR-Cas系统开发的单碱基编辑在治疗基因组点突变引起的遗传疾病方面显示出巨大潜力。碱基编辑器中使用的脱氨酶都是单链DNA脱氨酶,在Cas9和sgRNA的作用下,目标DNA双链中的非靶向链暴露出来,为单链DNA脱氨酶实现有效碱基转换提供了必要条件4。与CRISPR-Cas系统相比,锌指蛋白(ZF)和转录激活因子样效应子(TALE)只具有结合DNA双链的活性,却无法解开DNA双链5。因此,简单将单链DNA脱氨酶与ZF或TALE结合无法实现对DNA的有效碱基编辑6。
2020年,Joseph Mougous实验室和David Liu实验室利用一种能够作用于双链DNA的脱氨酶DddA开发出了线粒体单碱基编辑器,首次实现了线粒体基因C->T的碱基编辑7。2022年Jin-Soo Kim实验室使用DddA和TadA8e组合,进一步实现了线粒体基因组A->G的碱基编辑8。然而,左二伟实验室和伊成器实验室随后发现DddA系统存在比较严重的脱靶效应9,10,特别是DddA与CTCF存在相互作用,会产生细胞核基因组的非特异性编辑10。
2023年5月22日,北京大学蛋白质与植物基因研究国家重点实验室魏文胜课题组在Nature Biotechnology杂志在线发表题为 “Strand-selective base editing of human mitochondrial DNA using mitoBEs” 的研究论文,报道了一种名为mitoBEs的全新线粒体单碱基编辑工具,该工具不依赖于DddA系统。mitoBEs不仅能够高效地实现A->G或C->T的单碱基编辑,还具备选择性地编辑特定链的能力,这是DddA系统所不具备的。此外,研究人员未观察到明显的脱靶现象。
由于目前发现的除DddA之外的DNA脱氨酶,都只能作用于单链DNA,整个研究基于这样的假设:在靶向位点产生瞬时的单链DNA,可以为所有“普通” 脱氨酶提供有效反应底物。因此,在TALE系统提供靶向的基础上,研究者整合了切口酶(nickase)和脱氨酶(deaminase),成功建立了高效的TALE版本的单碱基编辑器,实现了线粒体基因组的碱基编辑(mitochondrial DNA base editors, mitoBEs)。使用含有线粒体定位信号的TALE-MutH和TALE-TadA8e(V106W)靶向线粒体基因组,可以实现有效的A->G编辑(图1)。对切口酶MutH的突变研究,可以大幅度突破其序列偏好,将可编辑范围提高10倍以上。此外,无识别序列偏好的切口酶Nt.BspD6I(C)和FokI-FokI(D450A),也能够有效应用于mitoBEs系统(图2)。
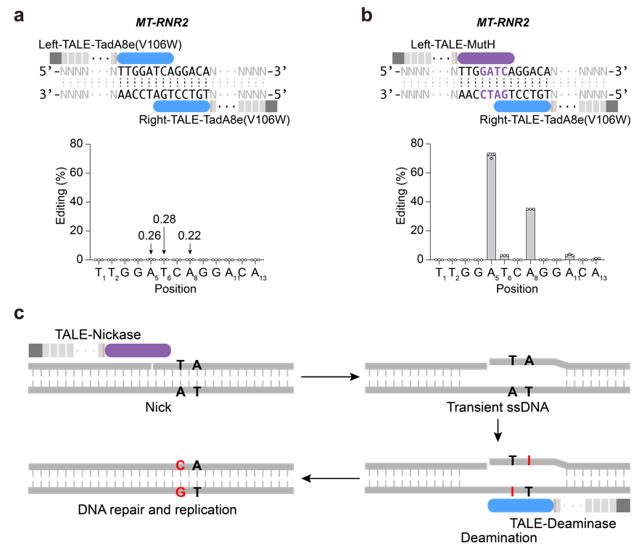
图1:引入nickase来实现链选择性DNA编辑及mitoBE工作模型
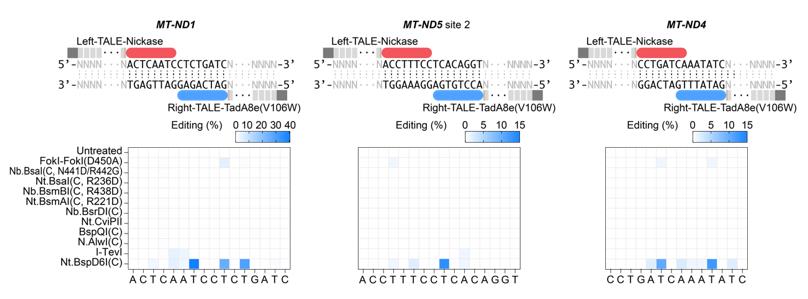
图2:筛选可以用于mitoBE系统的无识别序列限制的nickase
除了A->G方向的编辑,TALE-MutH和TALE-rAPOBEC1-2×UGI的结合可以实现C->T的高效碱基转换。与DdCBE相比,mitoBEs具有链选择性偏好。此外,通过全基因组测序,mitoBEs在线粒体和细胞核中都没有检测到严重的脱靶编辑,证明其具有高度特异性和安全性。
研究者进一步尝试这一新型编辑器在疾病治疗中的应用。Leber遗传性视神经病变(Leber's hereditary optic neuropathy, LHON)是一种由线粒体基因突变引起的急性眼部疾病,患者均为成年人。研究者利用环状RNA编码的mitoBEs实现了高效线粒体DNA链选择性碱基编辑,成功建立了疾病模型。随后,针对LHON患者来源的细胞,使用环状RNA编码的mitoBEs在目标位点实现了约20%的编辑效率,修复后的细胞具有更高的ATP含量和氧化呼吸水平,表明mitoBEs对线粒体遗传疾病具有治疗潜力。这是首次通过碱基编辑方式修正了线粒体的致病突变(图3)。由于理论上这一新技术能够修正大多数线粒体疾病突变(图3),这就为治疗这些危害重大的疾病提供了有希望的治疗方法。此外,该技术方案也适用于细胞核基因组的碱基编辑,对相关疾病治疗提供了潜力巨大的新工具。
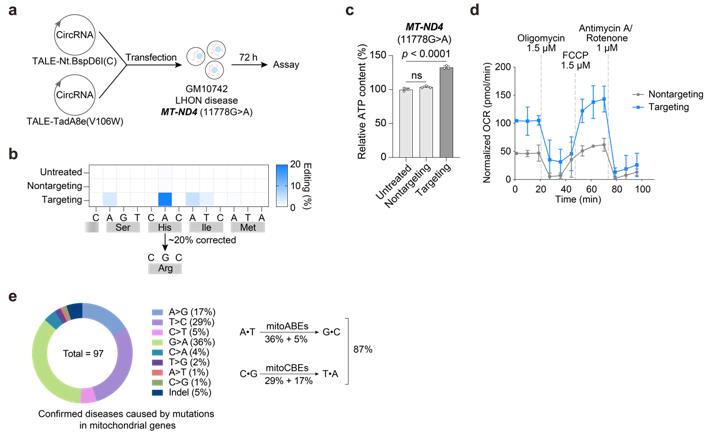
图3:使用mitoBE纠正LHON病人来源细胞的线粒体基因突变
北京大学魏文胜课题组博士后伊宗裔、博士研究生张小雪为论文的共同第一作者,唐玮、于莹、魏晓旭和张雪对文章也作出了重要贡献。该研究项目得到了国家重点研发计划、国家自然科学基金重点项目、北京市科委生物医学前沿创新推进项目、北大-清华生命科学联合中心、昌平实验室和中国博士后科学基金的支持。
文章链接: https://doi.org/10.1038/s41587-023-01791-y
1. Gammage, P. A., Moraes, C. T. & Minczuk, M. Mitochondrial Genome Engineering: The Revolution May Not Be CRISPR-Ized. Trends Genet 34, 101-110, doi:10.1016/j.tig.2017.11.001 (2018).
2. Bacman, S. R.et al. MitoTALEN reduces mutant mtDNA load and restores tRNA(Ala) levels in a mouse model of heteroplasmic mtDNA mutation. Nat Med 24, 1696-1700, doi:10.1038/s41591-018-0166-8 (2018).
3. Gammage, P. A. et al. Genome editing in mitochondria corrects a pathogenic mtDNA mutation in vivo. Nat Med 24, 1691-1695, doi:10.1038/s41591-018-0165-9 (2018).
4. Anzalone, A. V., Koblan, L. W. & Liu, D. R. Genome editing with CRISPR-Cas nucleases, base editors, transposases and prime editors. Nat Biotechnol 38, 824-844, doi:10.1038/s41587-020-0561-9 (2020).
5. Deng, D. et al. Structural basis for sequence-specific recognition of DNA by TAL effectors. Science 335, 720-723, doi:10.1126/science.1215670 (2012).
6. Yang, L. et al. Engineering and optimising deaminase fusions for genome editing. Nat Commun 7, 13330, doi:10.1038/ncomms13330 (2016).
7. Mok, B. Y. et al. A bacterial cytidine deaminase toxin enables CRISPR-free mitochondrial base editing. Nature 583, 631-637, doi:10.1038/s41586-020-2477-4 (2020).
8. Cho, S. I. et al. Targeted A-to-G base editing in human mitochondrial DNA with programmable deaminases. Cell 185, 1764-1776 e1712, doi:10.1016/j.cell.2022.03.039 (2022).
9. Wei, Y. et al. Mitochondrial base editor DdCBE causes substantial DNA off-target editing in nuclear genome of embryos. Cell Discov 8, 27, doi:10.1038/s41421-022-00391-5 (2022).
10. Lei, Z. et al. Mitochondrial base editor induces substantial nuclear off-target mutations. Nature 606, 804-811, doi:10.1038/s41586-022-04836-5 (2022).
- 陆剑研究组合作开发免疫印迹数学模型DynaVac,定量指导疫苗更新与接种策略2026.04.20
- 汪阳明团队开发REDDIT技术,实现增强子RNA与多类非编码RNA转录的高灵敏动态监测2026.04.20
- 陆剑课题组揭示果蝇上游开放读码框的演化规律与补偿机制2026.03.27
- 魏文胜课题组受邀综述:利用碱基与引导编辑器实现疾病相关变异的大规模解码2026.03.23
- 焦雨铃研究组构建禾本科花序发育数学模型,指导小麦高产基因挖掘2026.03.16
- 何爱彬团队与合作者开发新一代表观液体活检平台实现疾病组织器官精准溯源2026.03.05
- 陈雪梅教授课题组揭示新型RNA帽子修饰的跨物种分布与动态调控2026.03.05
- 肖俊宇团队与赵明辉、谭颖团队合作揭示补体系统C3转化酶组装及识别底物C3的分子机制2026.02.21
- 钟声课题组鉴定到拟南芥隔膜处“阻止多花粉管穿出”受体复合物的新组分2026.02.11
- 钟声研究员与瞿礼嘉院士合作揭示被子植物两次受精事件对受精补偿效率的关键作用2026.02.11
- 陈雪梅研究组揭示RdDM通路在作物免疫调控中的新功能,为大豆抗病改良提供了潜在的新思路、新靶点2026.02.10
- 秦跟基课题组揭示调控种子大小的新机制2026.02.10
- 罗述金课题组古DNA研究揭示:日本晚更新世并无虎,而为洞狮2026.01.27
- 张蔚课题组与合作者揭秘蜘蛛纺器起源2026.01.15
- 伊成器研究组报道AIM平台,突破“单点编辑”限制,实现RNA多位点、多功能精准操控2026.01.07
- 田望课题组发现植物抗逆“全能选手”,为提高植物“钙营养”和复合逆境抗性提供新概念2026.01.06
- 张蔚课题组与合作者揭示红珠凤蝶马兜铃酸抗性机制2026.01.05
- 刘君团队开发FOCAS平台实现m6A修饰位点的全转录组功能解析2026.01.05
- 肖俊宇研究组揭示FcRL5受体识别 IgG的分子机制2026.01.02
- 王伟课题组报道应激颗粒实现胞内氧化还原异质性的新功能:细胞抗氧化的“智能调控枢纽”2025.12.22
- 李晟课题组与合作者揭示保护地缓解人类对兽类行为干扰的关键作用2025.12.15
- 姚蒙研究组系统评估无脊椎动物宏条形码引物,助力eDNA生物多样性研究2025.12.12
- 朱丹萌课题组与合作者揭示PICKLE调控染色质状态与基因转录的分子机理2025.12.09
- 季雄团队提出FeaSion策略揭示RNA聚合酶磷酸化的特征调控与功能2025.12.01
- 罗述金课题组古DNA研究揭示:豹猫与人共栖3500年直至汉末,家猫经丝绸之路唐代方始传入2025.11.28
- 白洋研究员入选第三期 “新基石研究员项目”资助名单2025.11.26
- 实验室主任瞿礼嘉教授2025年新当选中国科学院院士2025.11.25
- 汪阳明团队与西湖大学卢培龙团队利用人工智能辅助蛋白质设计实现精准线粒体DNA碱基编辑2025.11.18
- 肖俊宇和高宁团队联合发表多聚抗体设计策略2025.11.07
- 赵进东课题组应邀撰写藻胆体的结构和能量传递机制长文综述2025.10.28
- 郑晓峰课题组揭示代谢酶ALDOA入核激活NF-κB信号通路驱动胰腺癌进展2025.10.23
- 陆剑课题组揭示果蝇饥饿耐受的遗传架构和性别差异2025.09.29
- 遇赫课题组揭示中国家猪的起源传播与人群互动过程2025.09.26
- 季雄团队揭示INO80/SWR复合物通过BRD2和染色质景观调控Pol II转录起始2025.09.22
- 刘启昆课题组与合作者在Current Opinion in Plant Biology发文总结植物再生领域表观遗传调控的研究进展2025.09.18
- 钟上威课题组受邀发表植物光信号传导Tansley长文综述2025.09.16
- 姚蒙课题组研发新型空气eDNA采集器高效检测动植物多样性2025.09.11
- 焦雨铃研究组克隆了小麦粒重新基因,服务高产育种2025.09.02
- 魏文胜团队与合作者联合开发新型通用型CAR-T 疗法治疗血液系统恶性肿瘤2025.08.22
- 魏文胜团队开发RNA环化新方法2025.08.12
- 汪阳明团队创新双组学技术MAPIT-seq:在单细胞水平同时绘制RNA结合蛋白作用图谱与基因表达图谱的新利器2025.08.11
- 周岳课题组揭示拟南芥PRC1介导的H2Aub loop的形成机制及功能2025.08.11
- 贺新强课题组与周岳课题组合作揭示PRC2调控维管组织模式建立机制2025.08.11
- 苏晓东课题组揭示清道夫受体CD163识别底物的分子机制2025.07.23
- 陈雪梅课题组系统阐释植物miRNA成熟与功能调控机制2025.07.23
- 苏晓东课题组与合作者揭示AAV与新型受体(AAVR2)结合的分子机制2025.07.15
- 合成植物基因组2025.07.09
- 伊成器课题组与合作者建立RNA"暗码",升级生命语言2025.07.04
- 魏文胜团队系统揭秘人类基因组中“沉默突变”的功能性“低语”2025.06.26
- 肖俊宇团队与张永辉团队合作揭示嗜乳脂蛋白激活γδ T细胞的“分子钳”机制2025.06.12
- 昌增益课题组揭示蛋白质内源性(顺式)去组装元件调控细菌细胞分裂环(Z环)的动态形成2025.06.09
- 陆剑课题组揭示uORF在动物进化与发育中发挥“翻译减震器”调控作用的新机制2025.06.09
- 张蔚课题组与合作者揭示兰花螳螂程序性体色转变的分子机制及生态学意义2025.05.30
- 2025年“全国科技活动周”和“全国科技工作者日”活动2025.05.29
- 李川昀团队与合作者开发细胞通讯分析工具STCase,揭示肿瘤微环境中空间特异性通讯事件2025.05.29
- 伊成器课题组系统阐释假尿嘧啶修饰的功能与治疗应用新范式2025.05.27
- 瞿礼嘉/钟声团队应邀撰写被子植物雌-雄相互作用保证双受精成功综述2025.05.26
- 陆剑课题组与合作者共同揭示uORFs通过精细调节CLOCK蛋白的翻译参与果蝇昼夜节律及睡眠行为的调控机制2025.05.16
- 伊成器团队发展痕量样品m6A修饰定量测序方法2025.05.08
- 白洋团队联合多位顶尖科学家系统解析根际微生物组调控水稻分蘖的功能与机制2025.04.24
- 瞿礼嘉/钟声课题组发现植物传粉过程中“未雨绸缪”的“两步授粉”备份新机制,为作物逆境下的育性优化提供新思路2025.04.15
- 曾虎课题组应邀撰写综述:空间组学技术的研究进展2025.04.06
- 张迪课题组受邀综述蛋白质L-乳酰化的研究进展2025.04.04
- 苏晓东课题组揭示短序列锚定元件AE在DNA与蛋白质结合中的重要作用2025.03.31
- 魏文胜团队实现人类肿瘤免疫调控网络的单碱基精度解析2025.03.21
- 白洋团队构建全球首个作物根际"细菌+病毒"基因组数据库2025.03.13
- 季雄团队揭示RNA聚合酶亚基RPB7偶联磷酸酶CTDP1稳定Pol II并介导转录再起始2025.03.05
- 何爱彬团队利用全景单细胞组蛋白修饰实现胚胎发育谱系追踪2025.03.04
- 赵进东课题组揭示蓝细菌藻胆体与光系统II结合的新分子机制2025.02.17
- 高歌课题组提出面向大规模异质性空间转录组学切片的表征与解析新方法2025.02.12
- 周岳课题组揭示拟南芥雄性生殖细胞发育过程中染色质三维结构的动态变化过程及其重要作用2025.02.12
- 魏文胜团队发布新一代线粒体碱基编辑器助力建立疾病动物模型2025.01.23
- 贺新强课题组揭示木质部管状分子发育的microRNA调控网络2025.01.19
- 周岳课题组在Genome Biology发文揭示了拟南芥中启动子空间调控模式和喷泉结构形成机制2025.01.02
- 高歌课题组提出人类转录调控元件建模与相关非编码变异功能解析方法2025.01.02
- 魏文胜团队利用碱基编辑器筛选绘制DNA损伤应答功能元件图谱2024.12.16
- 秦跟基课题组揭示弱光下种子萌发调控新机制2024.12.05
- 刘启昆课题组开发了全新的植物细胞谱系追踪工具2024.11.26
- 周岳课题组揭示植物首个三维基因组结构蛋白及其调控机制2024.11.22
- 周岳课题组揭示植物特有的PWWP结构域蛋白调控基因表达的分子机制2024.11.22
- 国家重点实验室陈雪梅教授获得2024年度“求是杰出科学家奖”2024.11.08
- 秦跟基课题组应邀撰写品牌综述“Tansley insight”总结TCP转录因子在细胞器、细胞和器官命运决定中的重要功能2024.10.28
- 郑晓峰课组揭示USP1-ATF4-CD98hc调控ENKTL淋巴瘤患者耐药的新机制2024.09.30
- 肖俊宇课题组揭示IgM–CD5L复合物的分子机制2024.09.30
- 陆剑课题组揭示密码子使用偏好性对翻译调控的影响2024.09.30
- 魏文胜团队实现蛋白质组中丝氨酸、苏氨酸和酪氨酸位点的功能解析2024.09.24
- 王继纵/邓兴旺课题组合作解析植物光敏色素phyB光信号转导的机制2024.09.24
- 刘君/杨雪瑞课题组合作揭示m6A-cenRNA调控癌细胞着丝粒稳态的机制2024.09.23
- 伊成器教授荣获2024年“科学探索奖”2024.08.29
- 王伟课题组报道蛋白酶体调控SG稳态抵御高温胁迫的新机制2024.08.22
- 肖俊宇团队阐明IgE 高亲和力受体FcεRI 复合物的组装机制2024.08.22
- 朱玉贤院士团队发布首个棉花基因组完整图谱,阐述棉族独特折叠胚胎形成的分子与演化机制2024.08.16
- 李晴课题组报道了滞后链核小体组装和冈崎片段成熟的协同机制2024.08.13
- 魏文胜团队报道非脱氨酶依赖的嘧啶碱基编辑器TBE2024.08.03
- 李晴研究组与合作者报道真核DNA复制体介导的亲本组蛋白表观遗传信息继承新机制2024.08.02
- 张迪课题组与合作者共同报道区分蛋白质乳酰化修饰同分异构体的新方法2024.07.22
- 国际遗传工程和生物技术中心(ICGEB)总干事Lawrence Banks教授一行访问陆剑课题组2024.06.26
- 郭强课题组与合作者揭示Synaptophysin调控突触小泡生成与功能的机制2024.06.06
- 2024年全国科技周开放活动2024.05.28
- 李磊课题组解析miR408平衡植物生长和抗旱的分子机制2024.05.16